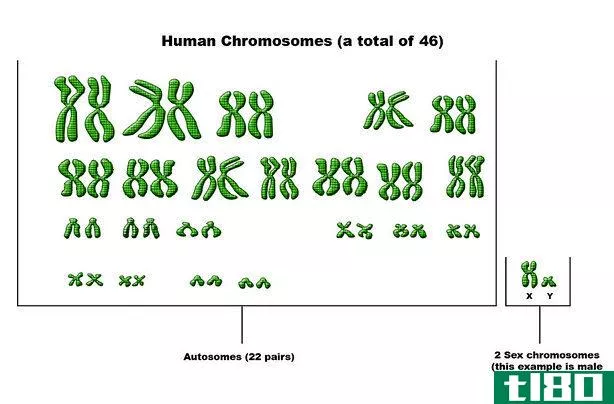
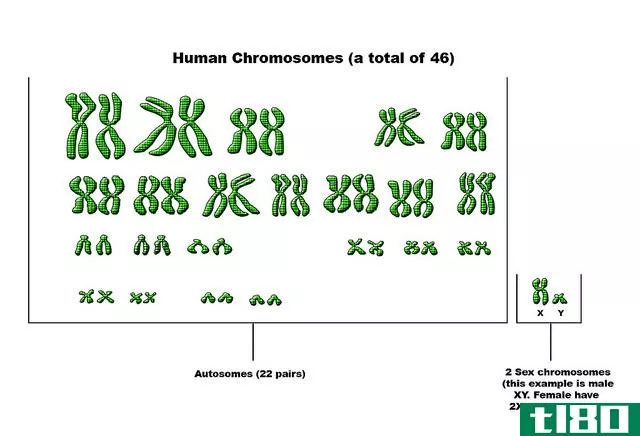
染色体行走(chromosome walking)和跳跃的(jumping)的区别
染色体行走和染色体跳跃是分子生物学中用于染色体上基因定位和基因组物理定位的两种技术手段。染色体行走是一种通过重复分离和克隆基因组文库中相邻克隆来克隆目标基因的技术。染色体跳跃是染色体行走的一种特殊形式,它克服了染色体行走的断点。染色体行走只能对较小长度的染色体进行排序和绘制,而染色体跳跃则可以对大部分染色体进行排序。这就是染色体行走和染色体跳跃的关键区别。
内容1。概述和主要区别2。什么是染色体行走3。什么是染色体跳跃。并排比较——染色体行走与跳跃5。摘要
什么是染色体行走(chromosome walking)?
染色体行走是一种利用重叠限制片段探索染色体未知序列区域的工具。在染色体行走过程中,一个已知基因的一部分被用作探针,并继续描述待绘制或测序的染色体的全长。从标记到目标长度。在染色体行走中,每个重叠片段的末端用于杂交,以识别下一个序列。
探针是从克隆的DN**段中制备出来的,并进行亚克隆。然后它们被用来寻找下一个重叠的片段。所有这些重叠序列被用来构建染色体的遗传图谱和定位目标基因。这是一种通过重组基因组文库中的重叠片段分析长片段DNA的方法。
染色体行走技术-步骤
- 分离含有已知基因或标记物的DN**段
- 制备所选片段的限制性图谱并对片段末端进行亚克隆以用作探针
- 探针与下一个重叠片段杂交
- 制备片段1的限制性图谱并对片段1的末端区域进行亚克隆,以用作识别下一个重叠片段的探针。
- 探针与下一个重叠片段2杂交
- 制备片段2的限制性图谱,并对片段2的末端进行亚克隆,作为下一个重叠片段鉴定的探针
以上步骤应持续到目标基因或序列全长的3'端。
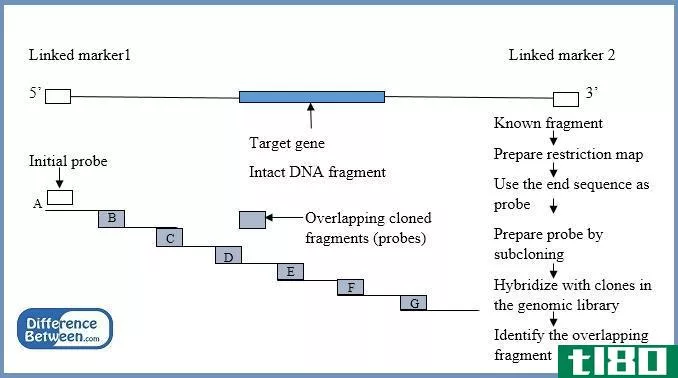
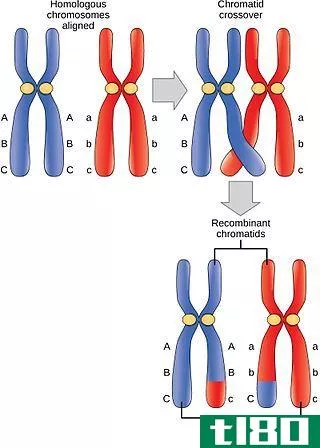
图01:染色体行走技术
染色体行走是细胞遗传学的一个重要方面,它可以发现许多生物体的snp,分析遗传性疾病和发现相关基因的突变。
什么是染色体跳跃(chromosome jumping)?
染色体跳跃是一种用于生物染色体定位的物理技术。这项技术是为了克服克隆过程中发现重复DNA区域而产生的染色体行走障碍。因此,染色体跳跃技术可以看作是染色体行走的一种特殊形式。与染色体行走相比,它是一种快速的方法,可以绕过染色体行走过程中不易克隆的重复DNA序列。染色体跳跃缩小了目标基因和已知的基因组图谱标记之间的差距。
染色体跳跃工具首先用特殊的限制性内切酶切割特定的DNA,然后将片段连接成环状环。然后用一个已知序列设计的引物对循环回路进行排序。这种引物能以另一种方式跳跃和排序。因此,它可以绕过重复的DNA序列,快速穿过染色体寻找目标基因。
囊性纤维化疾病基因编码的发现是通过染色体跳跃工具完成的。结合起来,染色体跳跃和行走可以增强基因组作图过程。
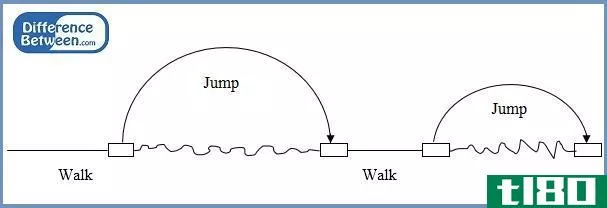
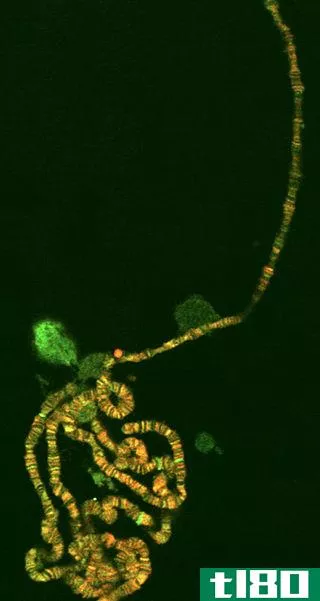
图02:染色体跳跃
染色体行走(chromosome walking)和跳跃的(jumping)的区别
| 染色体行走与跳跃 | |
| 染色体是分子生物学中用于基因组定位和定位特定基因的工具。 | 染色体跳跃是一种用于基因组物理定位和快速发现染色体中靶基因的工具。 |
| 序列比较长度 | |
| 只有很小的片段可以通过染色体行走来克隆。 | 较大长度的染色体可以通过染色体跳跃来绘制。 |
| 染色体重复DNA的克隆 | |
| 染色体行走技术很难在染色体中找到重复的DNA序列。 | 它可以绕过重复的DNA序列。因此,在测序过程中找到它们并不困难。 |
| 影响过程的因素 | |
| 这个过程的成功取决于基因组的大小以及从已知基因组位置到所需基因的距离。 | 成功与否并不取决于从标记到目标的距离的基因组大小。 |
| 未闭合DNA的影响 | |
| 染色体行走可以被未闭合的DN**段阻止。 | 皮科罗能演奏的最低音符是D4。 |
| 需要已知序列 | |
| 这个过程从目标附近的已知基因开始。 | 这个过程需要一个已知的片段来设计引物。 |
总结 - 染色体行走(chromosome walking) vs. 跳跃的(jumping)
当已知一个特定的基因位于染色体中先前克隆的基因附近,并且可以通过从基因组文库中重复分离相邻的基因组克隆来识别它时,染色体行走经常被应用。然而,当在染色体行走技术中发现重复的DNA区域时,这个过程就不能继续了。因此,这项技术突破了这一点。染色体跳跃是一种克服这一局限性的分子生物学工具。它绕过了这些难以克隆的重复DNA区域,有助于基因组的物理定位。行走和跳跃的主要区别是染色体跳跃。