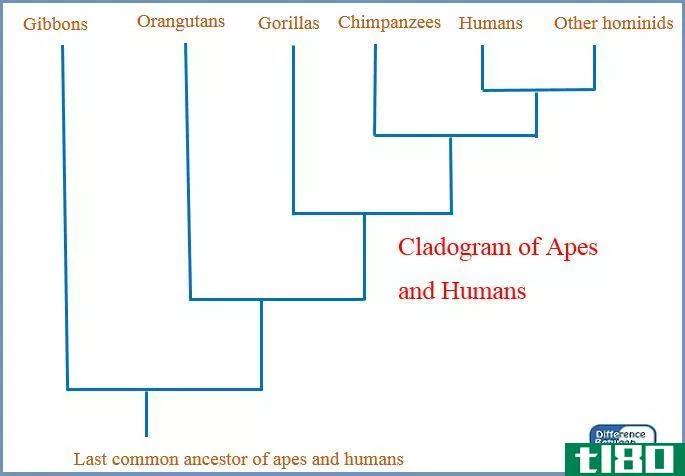
UPGMA和邻接连接树的关键区别在于每种方法产生的系统进化树的类型。UPGMA是构建有根系统发育树的技术,邻接连接树是构建无根系统发生树的技术。
系统发育树是一种树状图,显示了生物体之间的进化关系。一个系统进化树可以有不同的拓扑结构,这取决于构建树的技术。UPGMA和邻域连接树是构建系统进化树的两种主要方法。
目录
1. 概述和主要区别
2. 什么是UPGMA
3. 什么是邻接树
4. UPGMA与邻接树的相似性
5. 并排比较-UPGMA与表格形式的邻居连接树
6. 摘要
什么是upgma公司(upgma)?
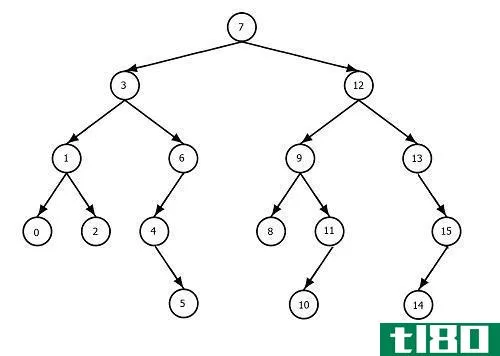
在生物信息学中,有不同的聚类技术。UPGMA代表未加权对组方法和算术平均数。它是一种分层分组方法。这种方法是由索卡尔和米切纳介绍的。这是发展系统进化树的最快技术。由此产生的系统发生树是一个有共同祖先的有根系统发生树。
当使用UPGMA方法绘制系统发生树时,它认为所有谱系的进化速率都是一样的。因此,UPGMA是一个重要的假设。然而,这也是该技术的主要缺点,因为在构建树的过程中没有考虑突变率。相反,它假设突变率是一个常数。此外,这一假说被称为“分子钟假说”。因此,在实际环境中,由UPGMA方法构建的系统发育树可能并不准确可靠。
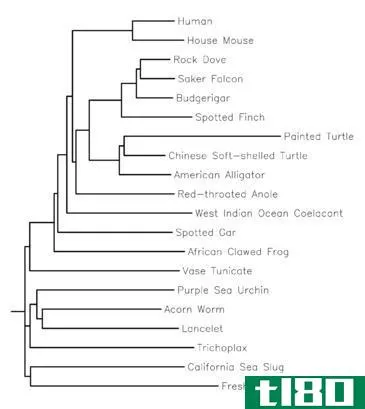
图01:UPGMA绘制的系统发育树
UPGMA方法考虑成对距离来生成系统发生树。最初,每一个物种都是一个集群,两个进化距离最小的集群形成一对。因此,它依赖于距离矩阵。算法表达式在解释使用UPGMA方法绘制的系统发育树的数据时起着重要作用。
什么是邻接连接树(neighbor joining tree)?
邻域连接树是另一种用于生成系统树的聚类技术。Naruya Saitou和Masatoshi Nei是介绍该方法的先驱。与UPGMA不同的是,这种技术可以生成无根树。此外,该方法中的聚类不依赖于超距离。然而,在构建系统进化树时,考虑了进化速率的变化。因此,使用这种技术绘制的树会有变化。因此,这种方法使用特殊的数学算法来评估这些变化。
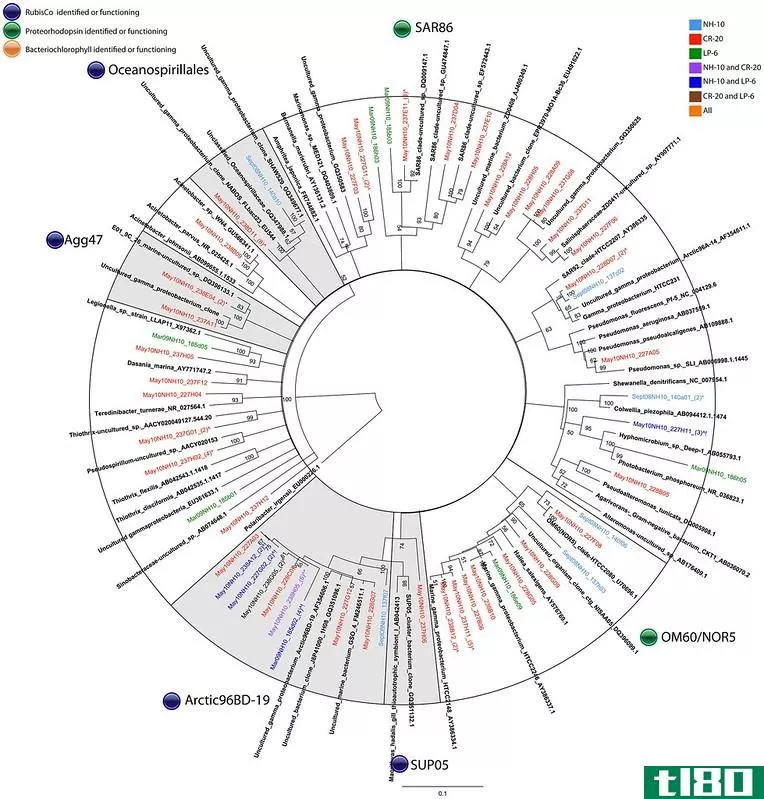
图02:从邻接法绘制的系统发育树
在构造树时,该方法分别考虑每个谱系之间的距离。每个血统连接树中新构造的节点。所有这些节点都连接到中心节点。因此,当一个新节点出现时,从中心节点到新节点的距离非常重要,并使用算法进行计算。这些算法数据决定了新节点的位置。
upgma公司(upgma)和邻接连接树(neighbor joining tree)的共同点
- 两种方法在构建系统进化树时都使用聚类技术。
- 此外,这两种方法都需要使用数学算法来解释系统发生树。
- DNA序列数据在这两种方法中都起着重要作用。
- 这两种方法都会产生自底向上的聚类方法。
- 此外,使用这两种技术可以分析大数据集。
- 使用bootstrap方法可以对这两种类型的树进行统计数据分析。
- 它们在生物的分类和鉴定中都起着重要的作用。
- 此外,这两种方法都提供了生物进化关系的数据。
upgma公司(upgma)和邻接连接树(neighbor joining tree)的区别
UPGMA与邻接连接树的关键区别在于所构造的树的类型。所以,UPGMA生成有根树,而邻接连接树生成无根树。此外,UPGMA是一种不太可靠的方法,而邻接树是一种比UPGMA更可靠的方法。所以,这是UPGMA和邻居连接树的另一个区别。
下面的信息图总结了UPGMA和邻居连接树之间的区别。
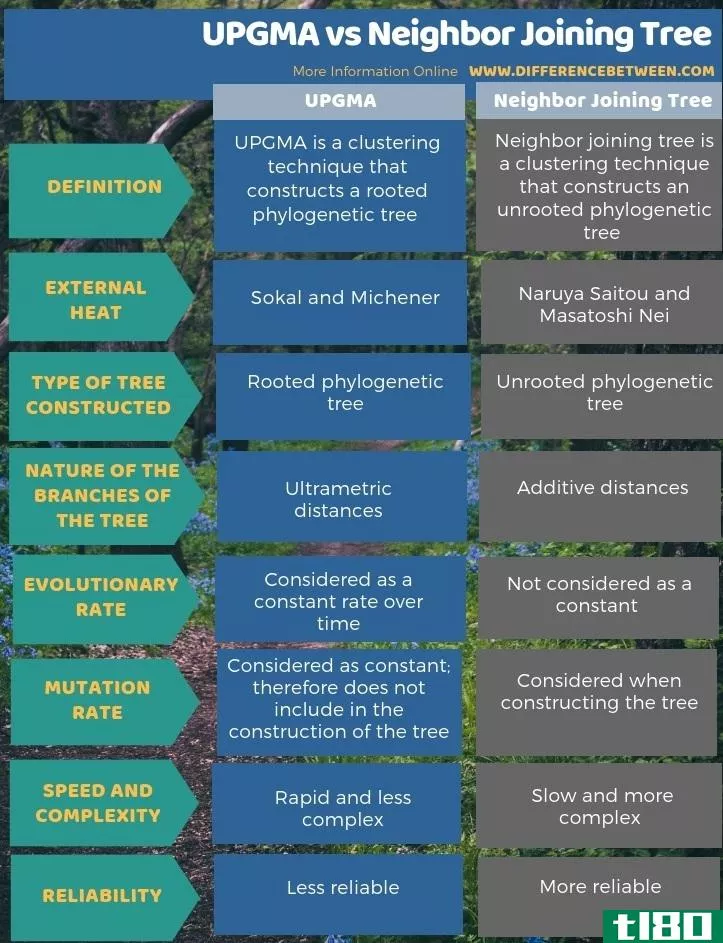
总结 - upgma公司(upgma) vs. 邻接连接树(neighbor joining tree)
UPGMA和邻域连接树方法是构建系统发生树的两种重要技术。UPGMA方法不考虑进化速率,而邻域连接方法在构建树时考虑了进化速率。因此,由NJ-tree方法得到的系统发育树具有较高的复杂性和可靠性。然而,它没有UPGMA方法那么快。此外,UPGMA和邻接连接树的关键区别取决于每种技术产生的树的类型。UPGMA生成有根的系统发育树,邻接连接树方法得到无根系统发育树。
引用
1.Pavlopoulos,Georgios A等人。“树分析和可视化的参考指南”,BioData Mining,BioMed Central,2010年2月22日,可在此处查阅。