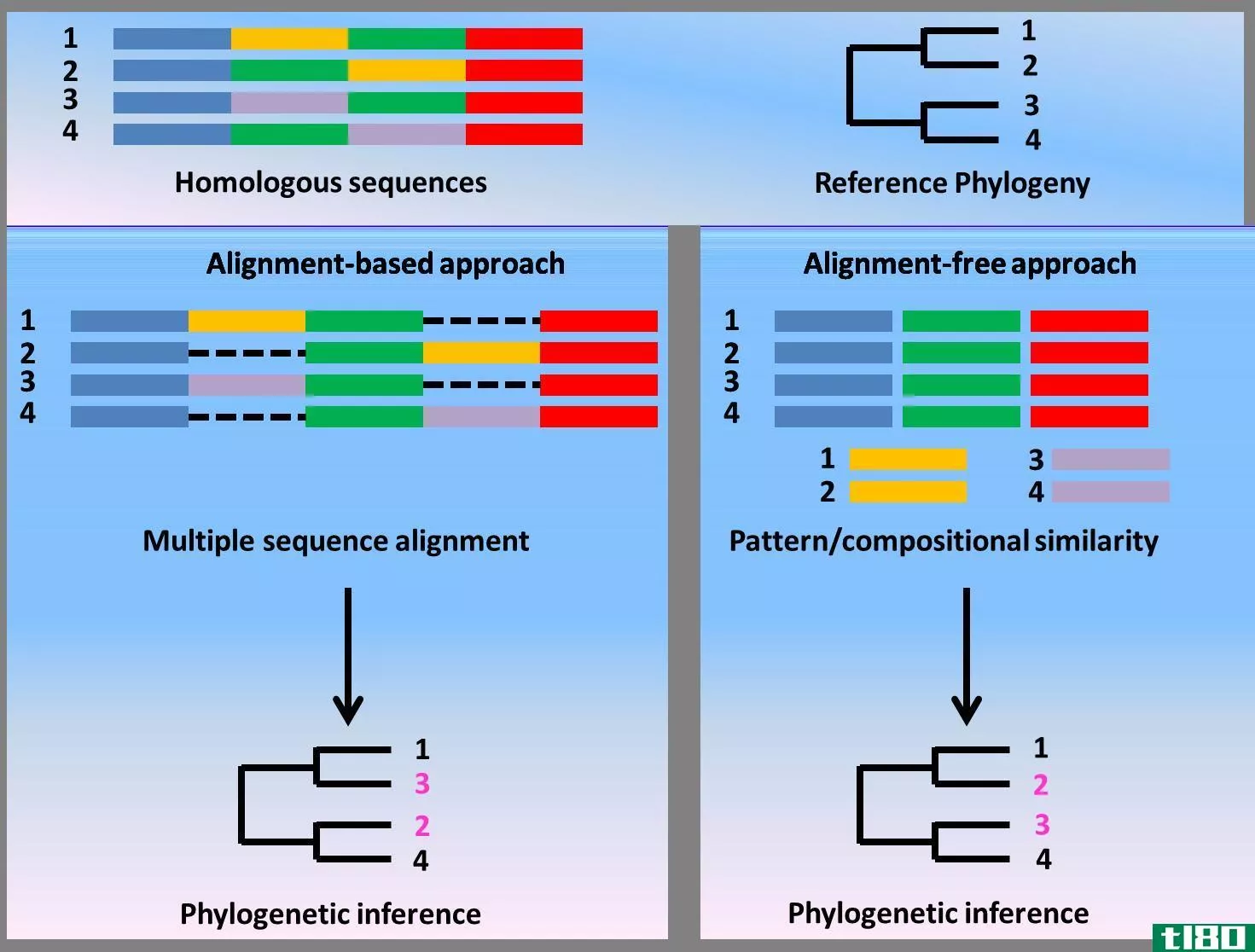
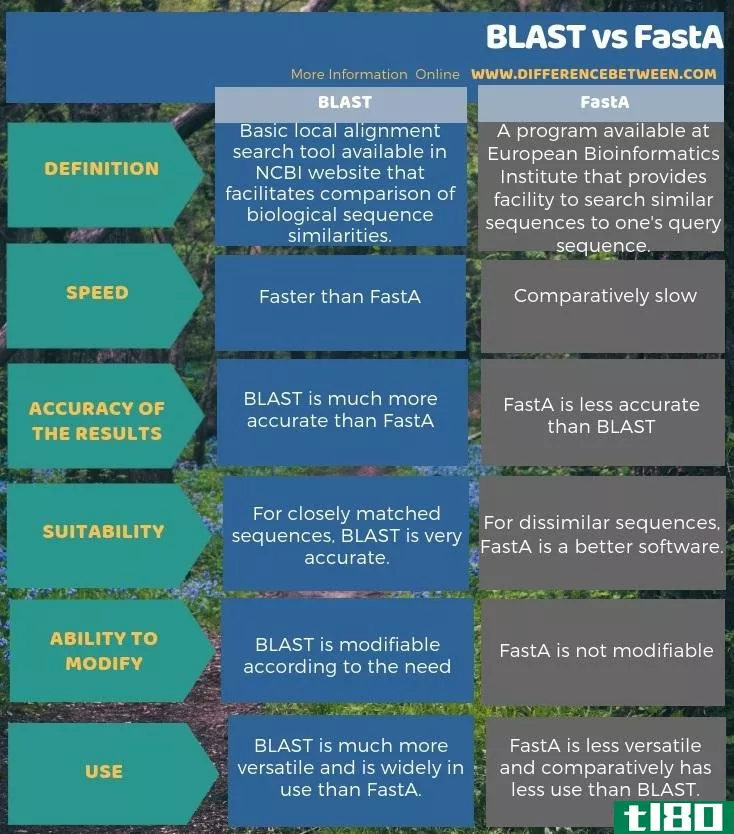
BLAST和FastA的主要区别在于BLAST是国家生物技术信息中心网站上的一个基本对齐工具,而FastA是一个可在欧洲生物信息学研究所网站上找到的相似性搜索工具。
BLAST和FastA是两个广泛使用的软件,用于比较不同物种的DNA、氨基酸、蛋白质和核苷酸的生物序列,并寻找它们的相似之处。这些算法都是在考虑速度的前提下编写的。因为,上世纪80年代中期,当科学家们能够在实验室中分离出DNA时,就提出了比较和找到相同基因的需求,以便在高速下进行进一步的研究。因此,这两个软件的开发使得用户可以用他们的查询序列快速搜索相似的序列。
BLAST是Basic Local Alignment Search Tool的缩写,它使用本地化方法比较两个序列。FastA是一个软件,指的是Fast a,其中a代表所有。在这里,该软件与字母表一起工作,如用于DNA测序的Fast A和用于蛋白质的Fast P。BLAST和FastA在比较任何基因组数据库方面都非常快,因此,在节省时间的同时,在经济上是非常可行的。
目录
1. 概述和主要区别
2. 什么是爆炸
3. 什么是FastA
4. BLAST和FastA的相似之处
5. 并列比较——BLAST与FastA的表格形式
6. 摘要
什么是爆炸(blast)?
BLAST是1990年开发的应用最广泛的生物信息学软件之一。从那时起,NCBI站点上的每个人都可以使用它。此外,任何人都可以访问并使用该软件。此外,BLAST是一种需要输入FastA格式数据或序列的软件。但是,它以纯文本、HTML或XML格式提供输出数据。BLAST的工作原理是搜索两个序列之间的局部相似性,并将相似序列短列表,然后搜索邻域相似性。

图01:爆炸结果
因此,该软件搜索大量相似的局部区域,并在达到阈值时给出结果。然而,这个过程不同于早期的软件,它先搜索整个序列,然后进行比较,因此花费了大量的时间。
除了上述相似性检查,BLAST还有许多其他用途,如DNA定位、比较不同物种的两个相同基因、创建系统发育树等。
什么是法斯塔(fasta)?
FastA是一个蛋白质序列比对软件。大卫·J·利普曼和威廉·R·皮尔森在1985年描述了这个软件。虽然这个软件最初只是用来比较蛋白质序列,但它的改进版也能比较DNA序列。在这里,这个软件使用的原理是寻找两个序列之间的相似性统计。它通过局部序列比对方法将DNA或蛋白质的一个序列与另一个序列相匹配。

图02:FastA
然而,它搜索局部区域以寻找相似性,而不是两个序列之间的最佳匹配。由于该软件有时会比较本地化的相似性,因此也会出现不匹配的情况。在一个序列中,FastA占用一小部分称为k元组,其中的元组可以是1到6,并与另一个序列的k元组相匹配。在匹配过程的最后,当它达到一个阈值时,它产生结果。
爆炸(blast)和法斯塔(fasta)的共同点
- BLAST和FastA是用于比较蛋白质和DNA序列相似性的生物信息学工具。
- 另外,两个程序都使用评分策略来比较序列。
- 此外,这两种工具都能产生非常精确的结果。
爆炸(blast)和法斯塔(fasta)的区别
BLAST是一种检查生物序列相似性的工具。另一方面,FastA是另一个促进蛋白质和DNA序列相似性检查的程序。然而,与FastA相比,BLAST软件非常受欢迎,因为它可以产生更准确和更快速的结果。因此,这就是BLAST和FastA之间的区别。此外,与FastA不同,BLAST程序可以根据用户的需要进行修改。因此,这是BLAST和FastA的另一个区别。
下面关于BLAST和FastA之间差异的信息图提供了更多细节。
总结 - 爆炸(blast) vs. 法斯塔(fasta)
BLAST和FastA是两个程序,允许用户将自己的查询序列与现有数据库中的序列进行比较并检查相似性。FastA最初的目的是比较蛋白质序列。但是,这个软件的改进版便于蛋白质和DNA序列的比较。尽管FastA是一个很好的软件,但大多数人使用BLAST对齐工具,因为它比FastA更受欢迎,并且产生更精确和更快速的结果。此外,爆炸工具可根据用户要求进行修改。简而言之,本文总结了BLAST和FastA的区别。
引用
1.马登,托马斯。“BLAST序列分析工具”,当前神经学和神经科学报告,美国国家医学图书馆,2013年3月15日。可在此处查阅